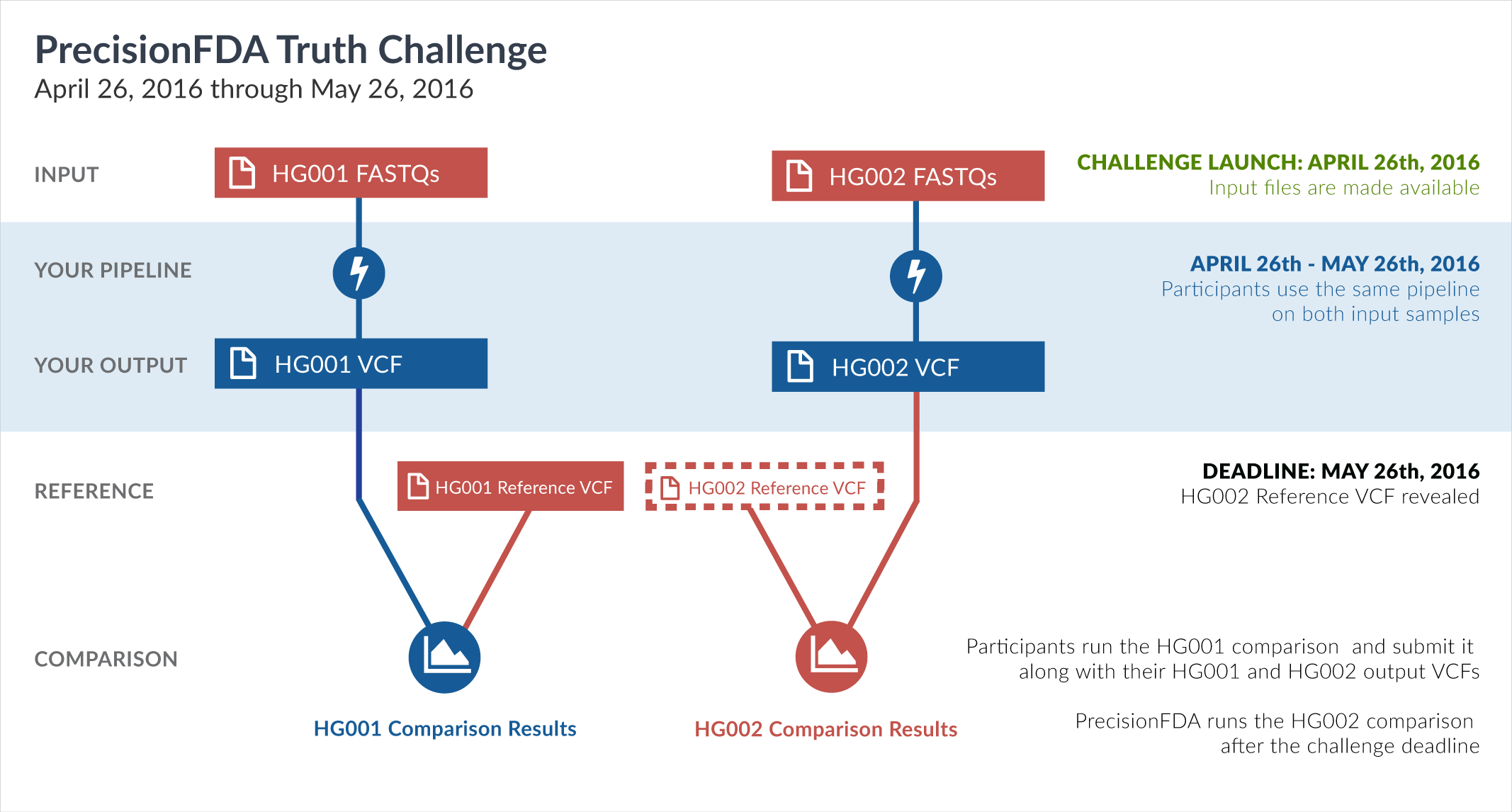
PrecisionFDA
Truth Challenge
Engage and improve DNA test results with our community challenges
Explore HG002 comparison results
Use this interactive explorer to filter all results across submission entries and multiple dimensions.
| Entry | Type | Subtype | Subset | Genotype | F-score | Recall | Precision | Frac_NA | Truth TP | Truth FN | Query TP | Query FP | FP gt | % FP ma | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
|
36651-36700 / 86044 show all | |||||||||||||||
| dgrover-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 95.8333 | 92.0000 | 100.0000 | 44.4444 | 23 | 2 | 25 | 0 | 0 | ||
| dgrover-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 96.2963 | 100.0000 | 92.8571 | 50.0000 | 13 | 0 | 13 | 1 | 1 | 100.0000 | |
| dgrover-gatk | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | * | 95.3020 | 94.6667 | 95.9459 | 64.9289 | 71 | 4 | 71 | 3 | 2 | 66.6667 | |
| dgrover-gatk | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | het | 96.2963 | 100.0000 | 92.8571 | 87.5000 | 13 | 0 | 13 | 1 | 0 | 0.0000 | |
| dgrover-gatk | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 95.7447 | 91.8367 | 100.0000 | 28.5714 | 45 | 4 | 45 | 0 | 0 | ||
| dgrover-gatk | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 92.8571 | 100.0000 | 86.6667 | 58.3333 | 13 | 0 | 13 | 2 | 2 | 100.0000 | |
| dgrover-gatk | INDEL | I16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | * | 85.7143 | 75.0000 | 100.0000 | 75.0000 | 3 | 1 | 3 | 0 | 0 | ||
| dgrover-gatk | INDEL | I16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | het | 50.0000 | 100.0000 | 1 | 1 | 0 | 0 | 0 | ||||
| dgrover-gatk | INDEL | I16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 100.0000 | 100.0000 | 100.0000 | 40.0000 | 2 | 0 | 3 | 0 | 0 | ||
| dgrover-gatk | INDEL | I16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| dgrover-gatk | INDEL | I1_5 | lowcmp_SimpleRepeat_triTR_51to200 | * | 96.0000 | 96.0000 | 96.0000 | 62.1212 | 24 | 1 | 24 | 1 | 0 | 0.0000 | |
| dgrover-gatk | INDEL | I1_5 | lowcmp_SimpleRepeat_triTR_51to200 | het | 80.0000 | 100.0000 | 66.6667 | 91.6667 | 2 | 0 | 2 | 1 | 0 | 0.0000 | |
| dgrover-gatk | INDEL | I1_5 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 97.7778 | 95.6522 | 100.0000 | 12.0000 | 22 | 1 | 22 | 0 | 0 | ||
| dgrover-gatk | INDEL | I1_5 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| dgrover-gatk | INDEL | D6_15 | lowcmp_SimpleRepeat_triTR_51to200 | * | 97.5038 | 96.4789 | 98.5507 | 46.9231 | 137 | 5 | 136 | 2 | 1 | 50.0000 | |
| dgrover-gatk | INDEL | D6_15 | lowcmp_SimpleRepeat_triTR_51to200 | het | 93.7037 | 95.8333 | 91.6667 | 76.6990 | 23 | 1 | 22 | 2 | 1 | 50.0000 | |
| dgrover-gatk | INDEL | D6_15 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 97.8947 | 95.8763 | 100.0000 | 24.3902 | 93 | 4 | 93 | 0 | 0 | ||
| dgrover-gatk | INDEL | D6_15 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 100.0000 | 100.0000 | 100.0000 | 38.2353 | 21 | 0 | 21 | 0 | 0 | ||
| dgrover-gatk | INDEL | I6_15 | lowcmp_SimpleRepeat_triTR_51to200 | * | 100.0000 | 100.0000 | 100.0000 | 69.7674 | 13 | 0 | 13 | 0 | 0 | ||
| dgrover-gatk | INDEL | I6_15 | lowcmp_SimpleRepeat_triTR_51to200 | het | 100.0000 | 100.0000 | 1 | 0 | 0 | 0 | 0 | ||||
| dgrover-gatk | INDEL | I6_15 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 100.0000 | 100.0000 | 100.0000 | 38.0952 | 12 | 0 | 13 | 0 | 0 | ||
| dgrover-gatk | INDEL | I6_15 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| dgrover-gatk | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | * | 100.0000 | 100.0000 | 100.0000 | 95.8333 | 9 | 0 | 9 | 0 | 0 | ||
| dgrover-gatk | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | het | 100.0000 | 100.0000 | 100.0000 | 95.0355 | 7 | 0 | 7 | 0 | 0 | ||
| dgrover-gatk | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| dgrover-gatk | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 100.0000 | 100.0000 | 100.0000 | 97.3333 | 2 | 0 | 2 | 0 | 0 | ||
| dgrover-gatk | SNP | ti | lowcmp_SimpleRepeat_triTR_51to200 | * | 100.0000 | 100.0000 | 100.0000 | 94.5205 | 8 | 0 | 8 | 0 | 0 | ||
| dgrover-gatk | SNP | ti | lowcmp_SimpleRepeat_triTR_51to200 | het | 100.0000 | 100.0000 | 100.0000 | 92.8571 | 6 | 0 | 6 | 0 | 0 | ||
| dgrover-gatk | SNP | ti | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| dgrover-gatk | SNP | ti | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 100.0000 | 100.0000 | 100.0000 | 96.7742 | 2 | 0 | 2 | 0 | 0 | ||
| dgrover-gatk | SNP | tv | lowcmp_SimpleRepeat_triTR_51to200 | * | 100.0000 | 100.0000 | 100.0000 | 98.5714 | 1 | 0 | 1 | 0 | 0 | ||
| dgrover-gatk | SNP | tv | lowcmp_SimpleRepeat_triTR_51to200 | het | 100.0000 | 100.0000 | 100.0000 | 98.2456 | 1 | 0 | 1 | 0 | 0 | ||
| dgrover-gatk | SNP | tv | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| dgrover-gatk | SNP | tv | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | C1_5 | lowcmp_SimpleRepeat_triTR_51to200 | * | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C1_5 | lowcmp_SimpleRepeat_triTR_51to200 | het | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C1_5 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C1_5 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | * | 94.5055 | 93.4783 | 95.5556 | 67.1533 | 43 | 3 | 43 | 2 | 2 | 100.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | het | 77.4194 | 75.0000 | 80.0000 | 92.1875 | 6 | 2 | 4 | 1 | 1 | 100.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 97.9592 | 96.0000 | 100.0000 | 42.2222 | 24 | 1 | 26 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 96.2963 | 100.0000 | 92.8571 | 50.0000 | 13 | 0 | 13 | 1 | 1 | 100.0000 | |
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | * | 96.6443 | 96.0000 | 97.2973 | 64.5933 | 72 | 3 | 72 | 2 | 1 | 50.0000 | |
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | het | 96.2963 | 100.0000 | 92.8571 | 87.5000 | 13 | 0 | 13 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 96.8421 | 93.8776 | 100.0000 | 25.8065 | 46 | 3 | 46 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 96.2963 | 100.0000 | 92.8571 | 60.0000 | 13 | 0 | 13 | 1 | 1 | 100.0000 | |
| ckim-vqsr | INDEL | C6_15 | lowcmp_SimpleRepeat_triTR_51to200 | * | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C6_15 | lowcmp_SimpleRepeat_triTR_51to200 | het | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C6_15 | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | C6_15 | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||