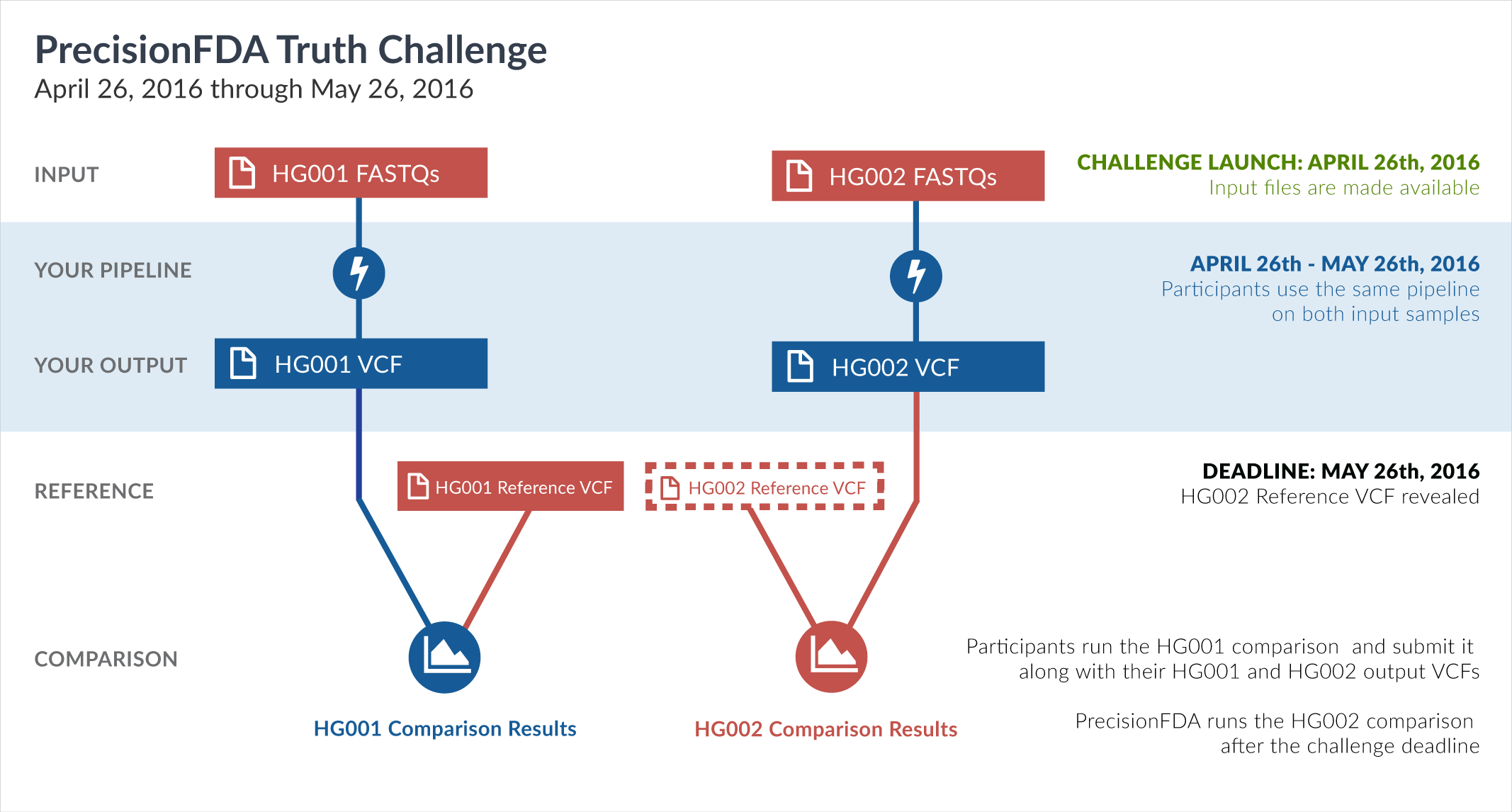
PrecisionFDA
Truth Challenge
Engage and improve DNA test results with our community challenges
Explore HG002 comparison results
Use this interactive explorer to filter all results across submission entries and multiple dimensions.
| Entry | Type | Subtype | Subset | Genotype | F-score | Recall | Precision | Frac_NA | Truth TP | Truth FN | Query TP | Query FP | FP gt | % FP ma | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
|
53751-53800 / 86044 show all | |||||||||||||||
| dgrover-gatk | INDEL | D6_15 | decoy | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.1379 | 1 | 0 | 1 | 0 | 0 | ||
| dgrover-gatk | INDEL | D6_15 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 98.0392 | 1 | 0 | 1 | 0 | 0 | ||
| dgrover-gatk | INDEL | D6_15 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 94.4444 | 1 | 0 | 1 | 0 | 0 | ||
| dgrover-gatk | INDEL | D6_15 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 66.6667 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 99.8487 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 87.5000 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | homalt | 50.0000 | 50.0000 | 50.0000 | 99.1111 | 1 | 1 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 99.8445 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 83.3333 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | homalt | 50.0000 | 50.0000 | 50.0000 | 99.1071 | 1 | 1 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l125_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.1538 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.4286 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.5517 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e1 | hetalt | 66.6667 | 50.0000 | 100.0000 | 96.5517 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | * | 66.6667 | 100.0000 | 50.0000 | 98.8235 | 1 | 0 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | het | 66.6667 | 100.0000 | 50.0000 | 98.5294 | 1 | 0 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.5915 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.5915 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | decoy | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.6933 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | decoy | homalt | 100.0000 | 100.0000 | 100.0000 | 99.9405 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.7742 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.1538 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | * | 100.0000 | 100.0000 | 100.0000 | 97.9167 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 96.9697 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_homopolymer_gt10 | * | 100.0000 | 100.0000 | 100.0000 | 99.9992 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_SimpleRepeat_homopolymer_gt10 | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.9919 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | map_l150_m0_e0 | hetalt | 66.6667 | 50.0000 | 100.0000 | 99.0654 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | map_l250_m1_e0 | hetalt | 50.0000 | 33.3333 | 100.0000 | 99.2647 | 1 | 2 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | map_l250_m2_e0 | hetalt | 50.0000 | 33.3333 | 100.0000 | 99.3902 | 1 | 2 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | map_l250_m2_e1 | hetalt | 50.0000 | 33.3333 | 100.0000 | 99.4048 | 1 | 2 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | segdupwithalt | * | 100.0000 | 100.0000 | 100.0000 | 99.9960 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | segdupwithalt | het | 100.0000 | 100.0000 | 100.0000 | 99.9946 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | decoy | * | 100.0000 | 100.0000 | 100.0000 | 99.9554 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | decoy | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.2647 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 98.0769 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 93.3333 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 75.0000 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D6_15 | tech_badpromoters | hetalt | 100.0000 | 100.0000 | 100.0000 | 0.0000 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_51to200bp_gt95identity_merged | homalt | 50.0000 | 100.0000 | 33.3333 | 95.0820 | 1 | 0 | 1 | 2 | 2 | 100.0000 | |
| ckim-vqsr | INDEL | I16_PLUS | map_l100_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.3077 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l125_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 88.8889 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l150_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 85.7143 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l150_m0_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 99.2424 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l150_m1_e0 | hetalt | 66.6667 | 50.0000 | 100.0000 | 94.7368 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l150_m2_e0 | hetalt | 66.6667 | 50.0000 | 100.0000 | 94.7368 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l150_m2_e1 | hetalt | 66.6667 | 50.0000 | 100.0000 | 94.7368 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | I16_PLUS | map_l250_m1_e0 | * | 66.6667 | 100.0000 | 50.0000 | 99.3333 | 1 | 0 | 1 | 1 | 0 | 0.0000 | |