PrecisionFDA
Truth Challenge
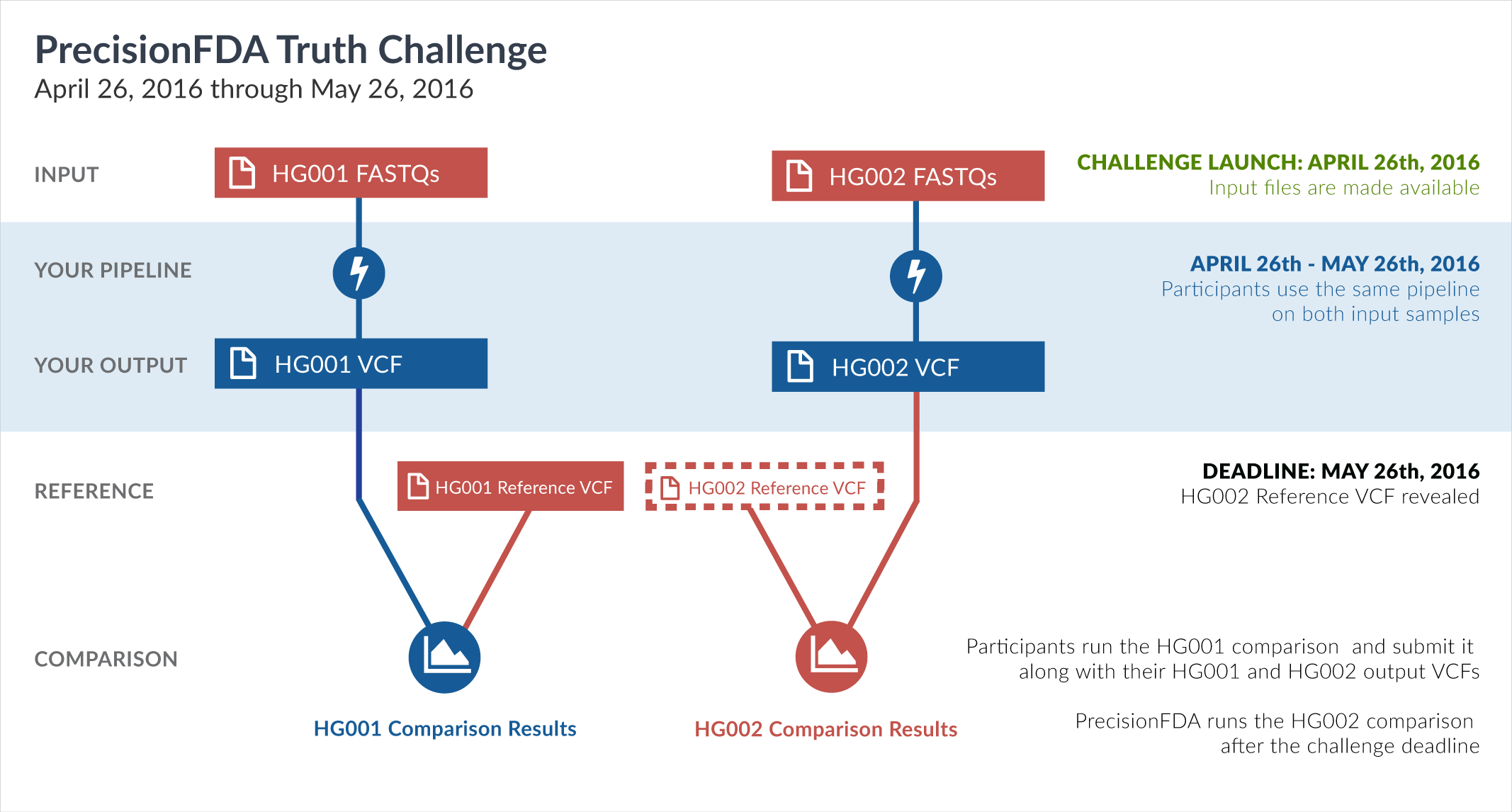
Engage and improve DNA test results with our community challenges
Explore HG002 comparison results
Use this interactive explorer to filter all results across submission entries and multiple dimensions.
| Entry | Type | Subtype | Subset | Genotype | F-score | Recall | Precision | Frac_NA | Truth TP | Truth FN | Query TP | Query FP | FP gt | % FP ma | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
|
73501-73550 / 86044 show all | |||||||||||||||
| astatham-gatk | INDEL | D16_PLUS | func_cds | het | 100.0000 | 100.0000 | 100.0000 | 81.3953 | 8 | 0 | 8 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | func_cds | homalt | 100.0000 | 100.0000 | 100.0000 | 76.4706 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | * | 100.0000 | 100.0000 | 100.0000 | 99.5460 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 99.8442 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.8571 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_AllRepeats_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 99.1111 | 2 | 0 | 2 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_51to200bp_gt95identity_merged | hetalt | 95.2381 | 90.9091 | 100.0000 | 84.8837 | 10 | 1 | 13 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | * | 100.0000 | 100.0000 | 100.0000 | 99.5338 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 99.8395 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 91.6667 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 99.1031 | 2 | 0 | 2 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt101bp_gt95identity_merged | hetalt | 97.2973 | 94.7368 | 100.0000 | 72.5000 | 18 | 1 | 22 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | het | 99.8145 | 99.6296 | 100.0000 | 63.2231 | 269 | 1 | 267 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | hetalt | 95.6522 | 91.6667 | 100.0000 | 45.8333 | 11 | 1 | 13 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_homopolymer_6to10 | hetalt | 100.0000 | 100.0000 | 100.0000 | 54.2857 | 12 | 0 | 16 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_homopolymer_gt10 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.0233 | 9 | 0 | 9 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_homopolymer_gt10 | homalt | 100.0000 | 100.0000 | 100.0000 | 97.6994 | 15 | 0 | 15 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_11to50 | hetalt | 100.0000 | 100.0000 | 100.0000 | 22.8571 | 51 | 0 | 54 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_11to50 | homalt | 100.0000 | 100.0000 | 100.0000 | 67.6259 | 45 | 0 | 45 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | lowcmp_SimpleRepeat_triTR_51to200 | hetalt | 95.8333 | 92.0000 | 100.0000 | 44.4444 | 23 | 2 | 25 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l100_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 90.5660 | 4 | 0 | 5 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l100_m1_e0 | hetalt | 91.6667 | 84.6154 | 100.0000 | 78.7037 | 22 | 4 | 23 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l100_m2_e0 | hetalt | 91.6667 | 84.6154 | 100.0000 | 79.1304 | 22 | 4 | 24 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l100_m2_e1 | hetalt | 90.9091 | 83.3333 | 100.0000 | 78.2258 | 25 | 5 | 27 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.5517 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m0_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 97.7011 | 2 | 0 | 2 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.1818 | 3 | 0 | 3 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m1_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.0583 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.6170 | 3 | 0 | 3 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.4127 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m2_e1 | hetalt | 85.7143 | 75.0000 | 100.0000 | 93.6170 | 3 | 1 | 3 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l125_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.4615 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l150_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.8750 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l150_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.8750 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l150_m2_e1 | hetalt | 66.6667 | 50.0000 | 100.0000 | 96.8750 | 1 | 1 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l250_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.7500 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l250_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l250_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.4127 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l250_m2_e1 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_l250_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.4127 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | map_siren | hetalt | 93.1034 | 87.0968 | 100.0000 | 82.7381 | 27 | 4 | 29 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | segdup | hetalt | 87.5000 | 77.7778 | 100.0000 | 93.1298 | 7 | 2 | 9 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | segdup | homalt | 100.0000 | 100.0000 | 100.0000 | 96.8586 | 12 | 0 | 12 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | tech_badpromoters | * | 100.0000 | 100.0000 | 100.0000 | 42.8571 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D16_PLUS | tech_badpromoters | het | 100.0000 | 100.0000 | 100.0000 | 0.0000 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D1_5 | decoy | * | 100.0000 | 100.0000 | 100.0000 | 99.9387 | 4 | 0 | 4 | 0 | 0 | ||
| astatham-gatk | INDEL | D1_5 | decoy | het | 100.0000 | 100.0000 | 100.0000 | 99.9567 | 2 | 0 | 2 | 0 | 0 | ||
| astatham-gatk | INDEL | D1_5 | decoy | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.6377 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D1_5 | decoy | homalt | 100.0000 | 100.0000 | 100.0000 | 99.9387 | 1 | 0 | 1 | 0 | 0 | ||
| astatham-gatk | INDEL | D1_5 | func_cds | * | 100.0000 | 100.0000 | 100.0000 | 40.7407 | 159 | 0 | 160 | 0 | 0 | ||