PrecisionFDA
Truth Challenge
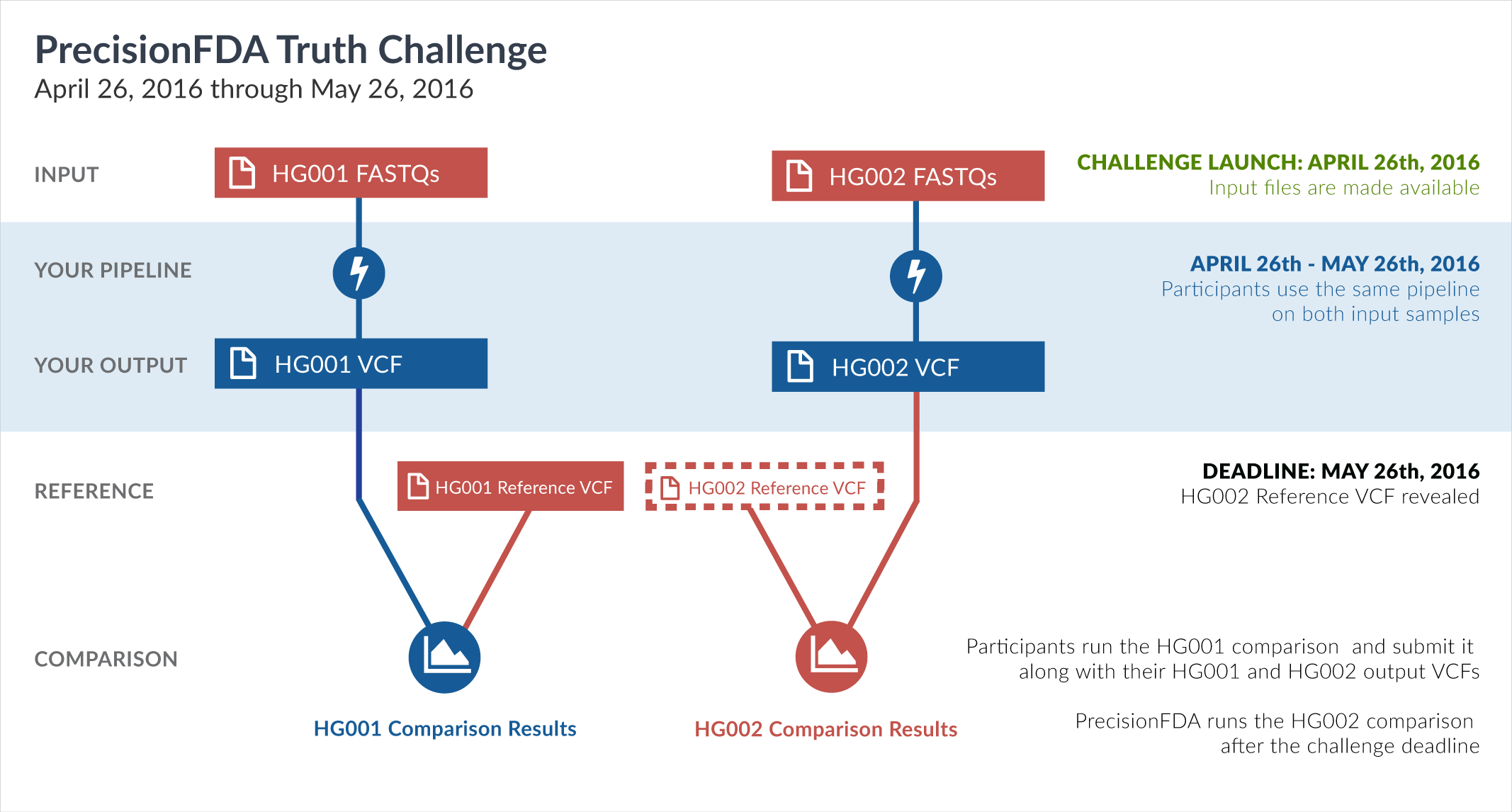
Engage and improve DNA test results with our community challenges
Explore HG002 comparison results
Use this interactive explorer to filter all results across submission entries and multiple dimensions.
| Entry | Type | Subtype | Subset | Genotype | F-score | Recall | Precision | Frac_NA | Truth TP | Truth FN | Query TP | Query FP | FP gt | % FP ma | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
|
5001-5050 / 86044 show all | |||||||||||||||
| ckim-dragen | INDEL | I1_5 | tech_badpromoters | homalt | 100.0000 | 100.0000 | 100.0000 | 59.3750 | 13 | 0 | 13 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | func_cds | het | 100.0000 | 100.0000 | 100.0000 | 46.6667 | 24 | 0 | 24 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 72.0824 | 122 | 0 | 122 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | lowcmp_SimpleRepeat_homopolymer_6to10 | homalt | 100.0000 | 100.0000 | 100.0000 | 81.2977 | 49 | 0 | 49 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | lowcmp_SimpleRepeat_homopolymer_gt10 | * | 100.0000 | 100.0000 | 100.0000 | 99.8634 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | lowcmp_SimpleRepeat_homopolymer_gt10 | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.3464 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | lowcmp_SimpleRepeat_triTR_11to50 | homalt | 100.0000 | 100.0000 | 100.0000 | 62.6582 | 59 | 0 | 59 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m0_e0 | * | 100.0000 | 100.0000 | 100.0000 | 96.5957 | 8 | 0 | 8 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m0_e0 | het | 100.0000 | 100.0000 | 100.0000 | 97.4026 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m0_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 93.9394 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.1053 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m1_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 95.1389 | 7 | 0 | 7 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.1818 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 95.7831 | 7 | 0 | 7 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m2_e1 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.4783 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l150_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 95.3757 | 8 | 0 | 8 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l250_m0_e0 | * | 100.0000 | 100.0000 | 100.0000 | 99.1525 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l250_m0_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 96.6667 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l250_m1_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 96.2500 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l250_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 96.5909 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | map_l250_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 96.7033 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | segdup | homalt | 100.0000 | 100.0000 | 100.0000 | 92.3328 | 47 | 0 | 47 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | tech_badpromoters | * | 100.0000 | 100.0000 | 100.0000 | 56.6667 | 13 | 0 | 13 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | tech_badpromoters | het | 100.0000 | 100.0000 | 100.0000 | 56.2500 | 7 | 0 | 7 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | tech_badpromoters | hetalt | 100.0000 | 100.0000 | 100.0000 | 50.0000 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | INDEL | I6_15 | tech_badpromoters | homalt | 100.0000 | 100.0000 | 100.0000 | 62.5000 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | SNP | * | func_cds | hetalt | 100.0000 | 100.0000 | 100.0000 | 64.2857 | 10 | 0 | 10 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt101bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 88.8889 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 83.3333 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_lt101bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 90.0000 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_lt51bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 88.8889 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_Human_Full_Genome_TRDB_hg19_150331_all_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.8571 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_diTR_11to50 | hetalt | 100.0000 | 100.0000 | 100.0000 | 95.2381 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_homopolymer_6to10 | hetalt | 100.0000 | 100.0000 | 100.0000 | 70.5882 | 5 | 0 | 5 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_quadTR_11to50 | hetalt | 100.0000 | 100.0000 | 100.0000 | 66.6667 | 5 | 0 | 5 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | * | 100.0000 | 100.0000 | 100.0000 | 94.7368 | 9 | 0 | 9 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | het | 100.0000 | 100.0000 | 100.0000 | 94.6970 | 7 | 0 | 7 | 0 | 0 | ||
| ckim-dragen | SNP | * | lowcmp_SimpleRepeat_triTR_51to200 | homalt | 100.0000 | 100.0000 | 100.0000 | 94.8718 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l100_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 79.4872 | 16 | 0 | 16 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l125_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 85.9375 | 9 | 0 | 9 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l150_m0_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.5455 | 3 | 0 | 3 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l250_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.2857 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l250_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.8272 | 5 | 0 | 5 | 0 | 0 | ||
| ckim-dragen | SNP | * | map_l250_m2_e1 | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.8272 | 5 | 0 | 5 | 0 | 0 | ||
| ckim-dragen | SNP | ti | func_cds | hetalt | 100.0000 | 100.0000 | 100.0000 | 57.8947 | 8 | 0 | 8 | 0 | 0 | ||
| ckim-dragen | SNP | ti | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt101bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 80.0000 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | ti | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 75.0000 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | ti | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_lt101bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 93.3333 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | ti | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRlt7_lt51bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.8571 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-dragen | SNP | ti | lowcmp_Human_Full_Genome_TRDB_hg19_150331_all_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 92.5926 | 2 | 0 | 2 | 0 | 0 | ||