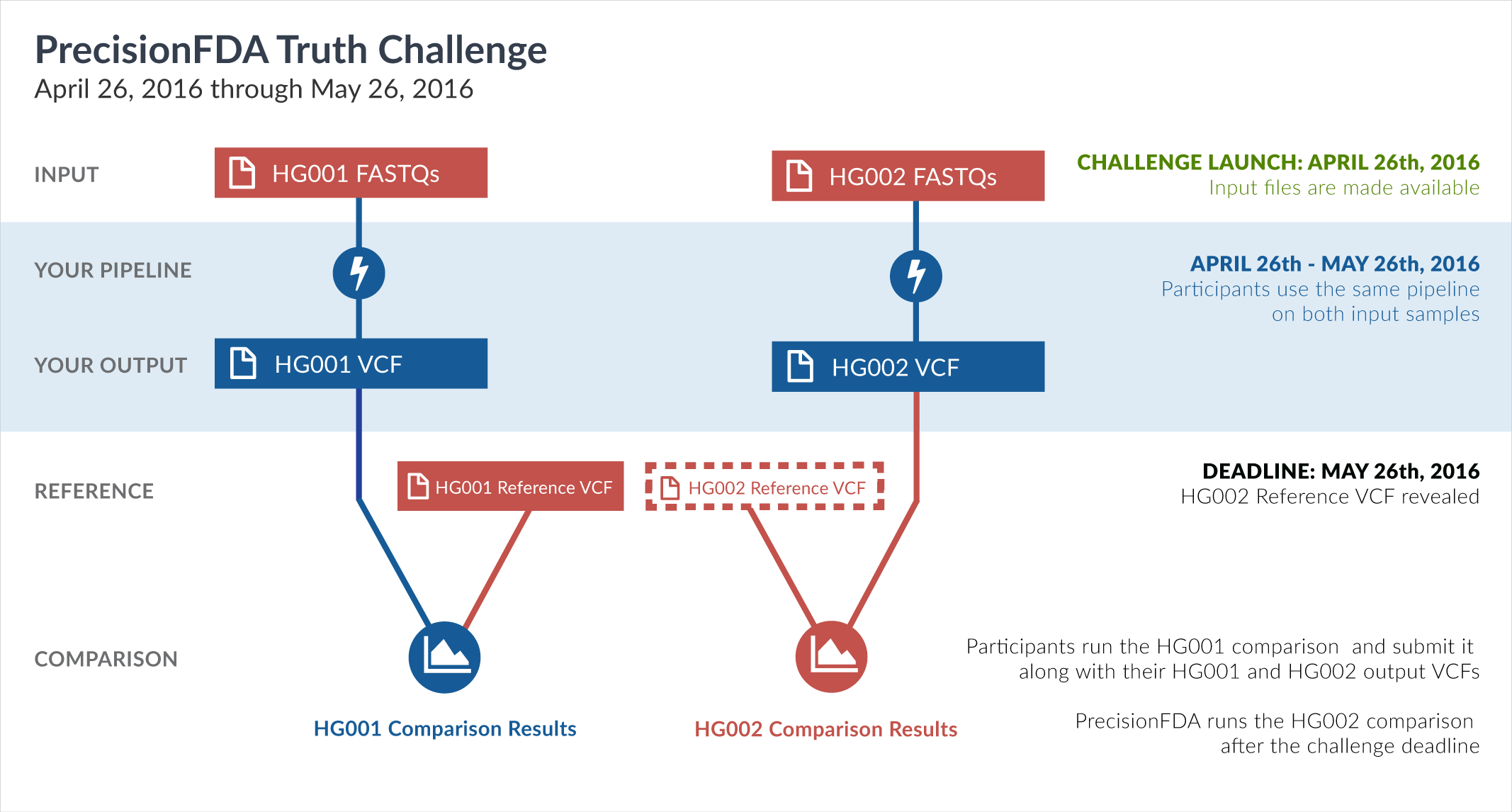
PrecisionFDA
Truth Challenge
Engage and improve DNA test results with our community challenges
Explore HG002 comparison results
Use this interactive explorer to filter all results across submission entries and multiple dimensions.
| Entry | Type | Subtype | Subset | Genotype | F-score | Recall | Precision | Frac_NA | Truth TP | Truth FN | Query TP | Query FP | FP gt | % FP ma | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
|
65401-65450 / 86044 show all | |||||||||||||||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e0 | homalt | 0.0000 | 0.0000 | 99.4083 | 0 | 0 | 0 | 1 | 0 | 0.0000 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e1 | * | 91.8919 | 94.4444 | 89.4737 | 97.9006 | 17 | 1 | 17 | 2 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e1 | het | 96.9697 | 100.0000 | 94.1176 | 97.5818 | 16 | 0 | 16 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e1 | hetalt | 66.6667 | 50.0000 | 100.0000 | 96.5517 | 1 | 1 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l150_m2_e1 | homalt | 0.0000 | 0.0000 | 99.4220 | 0 | 0 | 0 | 1 | 0 | 0.0000 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | * | 66.6667 | 100.0000 | 50.0000 | 98.8235 | 1 | 0 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | het | 66.6667 | 100.0000 | 50.0000 | 98.5294 | 1 | 0 | 1 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | hetalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m0_e0 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m1_e0 | * | 88.8889 | 100.0000 | 80.0000 | 98.5207 | 4 | 0 | 4 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m1_e0 | het | 85.7143 | 100.0000 | 75.0000 | 98.4906 | 3 | 0 | 3 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m1_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m1_e0 | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | * | 90.9091 | 100.0000 | 83.3333 | 98.5366 | 5 | 0 | 5 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | het | 85.7143 | 100.0000 | 75.0000 | 98.7578 | 3 | 0 | 3 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e0 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.5915 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | * | 90.9091 | 100.0000 | 83.3333 | 98.5507 | 5 | 0 | 5 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | het | 85.7143 | 100.0000 | 75.0000 | 98.7730 | 3 | 0 | 3 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | hetalt | 100.0000 | 100.0000 | 100.0000 | 94.1176 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_l250_m2_e1 | homalt | 100.0000 | 100.0000 | 100.0000 | 98.5915 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_siren | hetalt | 94.9153 | 90.3226 | 100.0000 | 80.7692 | 28 | 3 | 30 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | map_siren | homalt | 95.6522 | 97.0588 | 94.2857 | 94.7368 | 33 | 1 | 33 | 2 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D16_PLUS | segdup | hetalt | 87.5000 | 77.7778 | 100.0000 | 92.8000 | 7 | 2 | 9 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | segdupwithalt | * | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | segdupwithalt | het | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | segdupwithalt | hetalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | segdupwithalt | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D16_PLUS | tech_badpromoters | * | 100.0000 | 100.0000 | 100.0000 | 42.8571 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | tech_badpromoters | het | 100.0000 | 100.0000 | 100.0000 | 0.0000 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-vqsr | INDEL | D16_PLUS | tech_badpromoters | hetalt | 0.0000 | 0.0000 | 0.0000 | 0 | 0 | 0 | 0 | 0 | |||
| ckim-vqsr | INDEL | D16_PLUS | tech_badpromoters | homalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D1_5 | decoy | * | 100.0000 | 100.0000 | 100.0000 | 99.9751 | 4 | 0 | 4 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | decoy | het | 100.0000 | 100.0000 | 100.0000 | 99.9857 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | decoy | hetalt | 100.0000 | 100.0000 | 100.0000 | 99.6933 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | decoy | homalt | 100.0000 | 100.0000 | 100.0000 | 99.9405 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | func_cds | * | 99.6885 | 100.0000 | 99.3789 | 53.3333 | 159 | 0 | 160 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D1_5 | func_cds | het | 99.4220 | 100.0000 | 98.8506 | 62.8205 | 85 | 0 | 86 | 1 | 0 | 0.0000 | |
| ckim-vqsr | INDEL | D1_5 | func_cds | hetalt | 0.0000 | 100.0000 | 0 | 0 | 0 | 0 | 0 | ||||
| ckim-vqsr | INDEL | D1_5 | func_cds | homalt | 100.0000 | 100.0000 | 100.0000 | 32.7273 | 74 | 0 | 74 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | * | 100.0000 | 100.0000 | 100.0000 | 98.9141 | 11 | 0 | 11 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 98.7897 | 8 | 0 | 8 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.7742 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_AllRepeats_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 99.3769 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_51to200bp_gt95identity_merged | hetalt | 89.6000 | 81.1594 | 100.0000 | 52.5424 | 56 | 13 | 56 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | * | 100.0000 | 100.0000 | 100.0000 | 98.9648 | 10 | 0 | 10 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 98.8854 | 7 | 0 | 7 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | hetalt | 100.0000 | 100.0000 | 100.0000 | 96.1538 | 1 | 0 | 1 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_gt200bp_gt95identity_merged | homalt | 100.0000 | 100.0000 | 100.0000 | 99.3590 | 2 | 0 | 2 | 0 | 0 | ||
| ckim-vqsr | INDEL | D1_5 | lowcmp_Human_Full_Genome_TRDB_hg19_150331_TRgt6_lt51bp_gt95identity_merged | het | 100.0000 | 100.0000 | 100.0000 | 80.5621 | 657 | 0 | 657 | 0 | 0 | ||